A janela de varredura de parâmetros

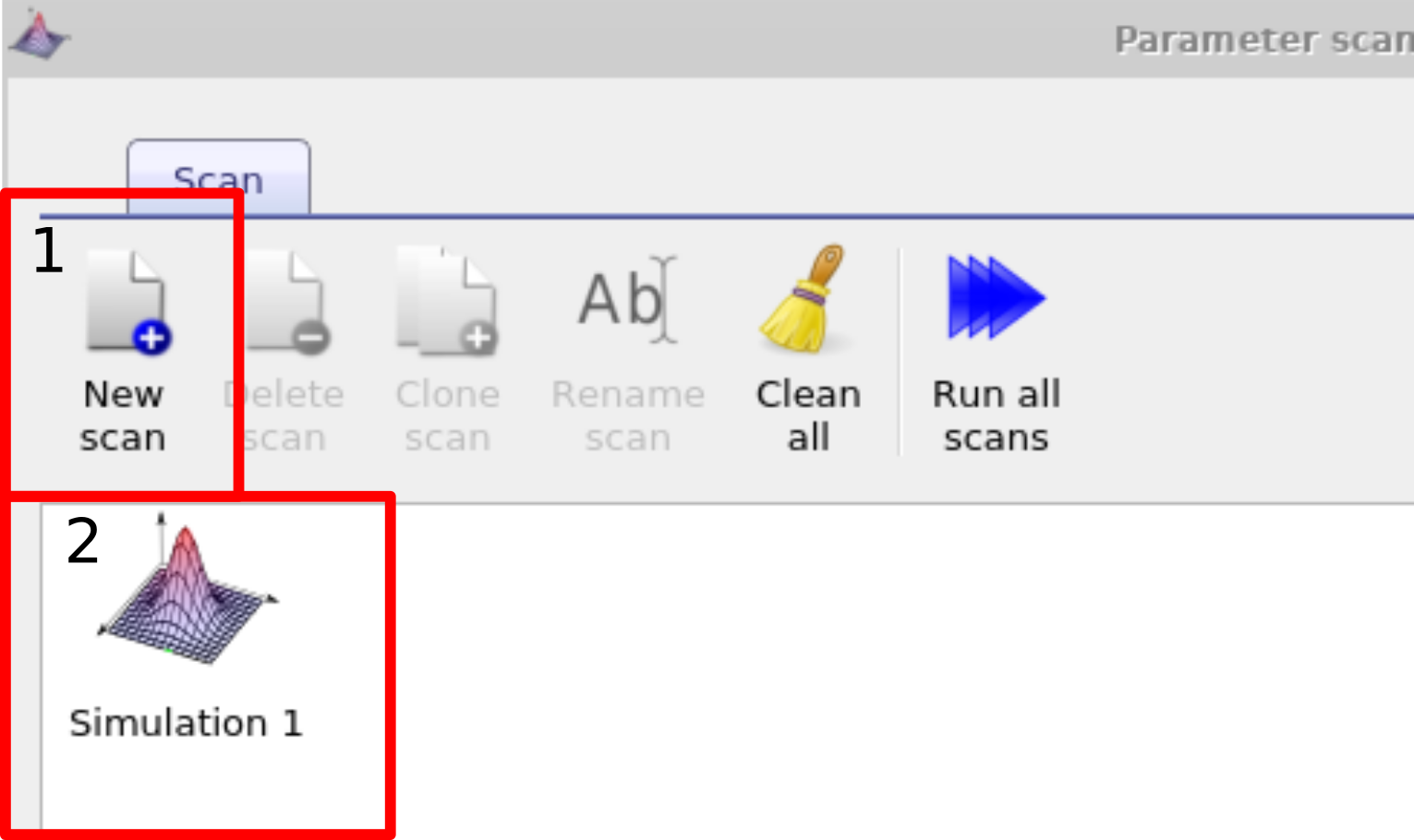
A forma mais direta de variar sistematicamente um parâmetro de simulação é utilizar a janela de varredura. Neste exemplo vamos alterar sistematicamente a mobilidade da camada ativa de uma célula solar PM6:Y6. Você pode encontrar este exemplo nas simulações de exemplo em Scripting and fitting/Scan demo (PM6:Y6 OPV). Após localizar esta simulação e abri-la, você deve abrir a janela de varredura de parâmetros. Isso pode ser feito clicando no ícone Parameter scan na faixa Automation (veja ??). Em seguida crie uma nova varredura clicando no botão new scan (1) (na simulação de exemplo isso já foi feito para você). Abra a nova varredura clicando duas vezes no ícone que representa a varredura (2), veja ??. Isso abrirá a janela de varredura, veja ??.
1. Selecionando um parâmetro para variar
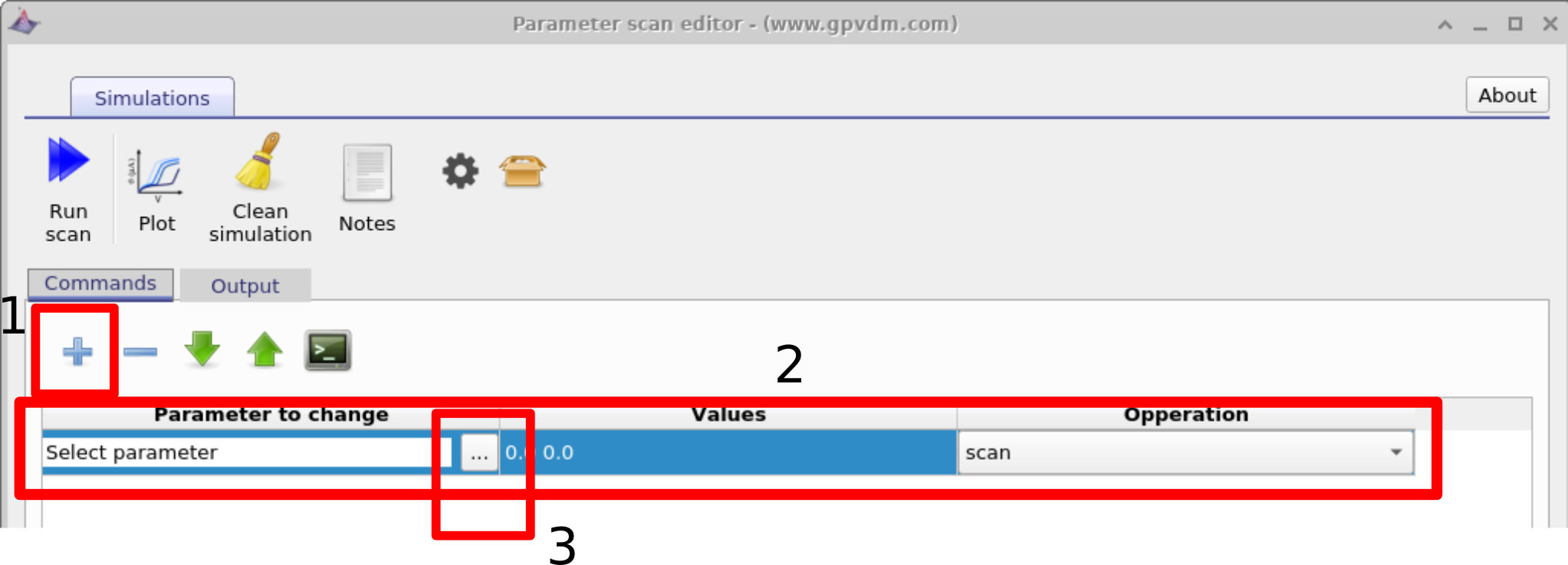
Depois que a janela de varredura for aberta, crie uma nova linha de varredura clicando no ícone de mais (1) na figura 17.1, selecione essa linha para que fique destacada (2), e então clique nos três pontos (3) para selecionar qual parâmetro deseja varrer. Novamente, se você estiver usando a simulação de exemplo, isso já terá sido feito.
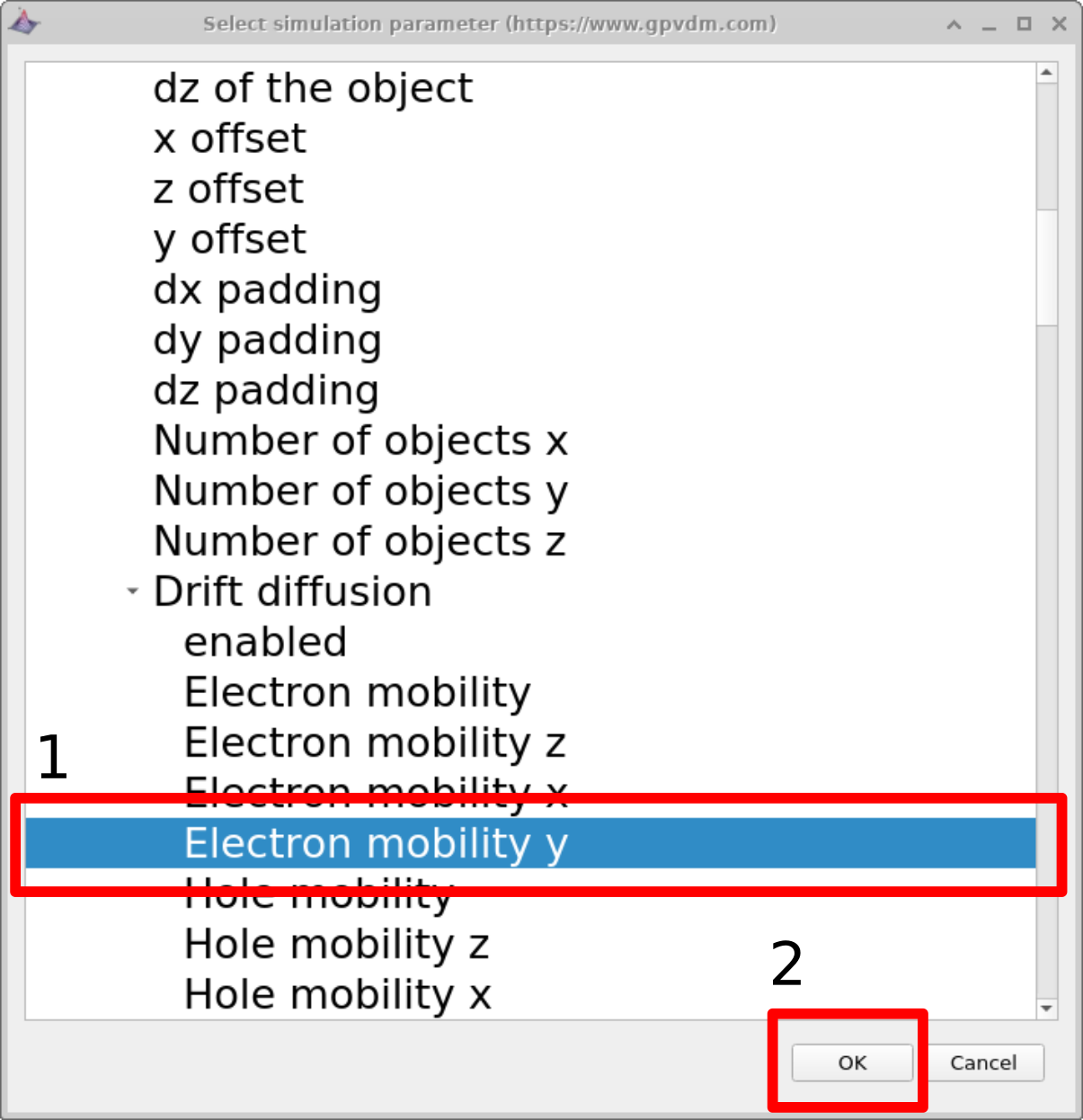
Neste exemplo, a mobilidade eletrônica de uma célula solar PM6:Y6 é selecionada para varredura. Isso é feito navegando até epitaxy\(\rightarrow\) PM6:Y6\(\rightarrow\) Drift diffusion\(\rightarrow\) Electron mobility y. Destaque o parâmetro e clique em OK. O parâmetro selecionado aparecerá então na lista de varredura. O significado de cada nível neste caminho de parâmetros é explicado abaixo:
-
epitaxy: Todos os parâmetros definidos no arquivo
.oghmasão expostos através da janela de seleção de parâmetros (veja [fig:scanselect]). A estrutura geral do dispositivo, incluindo suas camadas, é definida sob o cabeçalho epitaxy. -
PM6:Y6: Dentro de epitaxy, cada camada do dispositivo é identificada por nome. Neste exemplo, a camada ativa é chamada PM6:Y6. Se a camada ativa tivesse outro nome (por exemplo Perovskite ou P3HT:PCBM), esse nome de camada seria selecionado.
-
Drift diffusion: Todos os parâmetros de transporte elétrico associados a uma determinada camada são agrupados sob o subtítulo drift diffusion.
-
Electron mobility y: É possível definir mobilidades assimétricas nas direções z, x e y — isso é útil para simulações de OFET. No entanto, por padrão o modelo assume mobilidade simétrica igual em todas as direções. Esse valor é definido por Electron mobility y.
Embora este fluxo de trabalho possa parecer relativamente complexo no início, ele é essencialmente uma forma
estruturada de editar valores e caminhos dentro do arquivo JSON subjacente .oghma.
A janela de seleção de parâmetros simplesmente fornece uma interface gráfica para navegar e modificar este
arquivo de maneira segura e consistente.
Uma descrição detalhada da estrutura do arquivo pode ser encontrada na documentação em
o formato de arquivo do OghmaNano
.
2. Definindo os valores
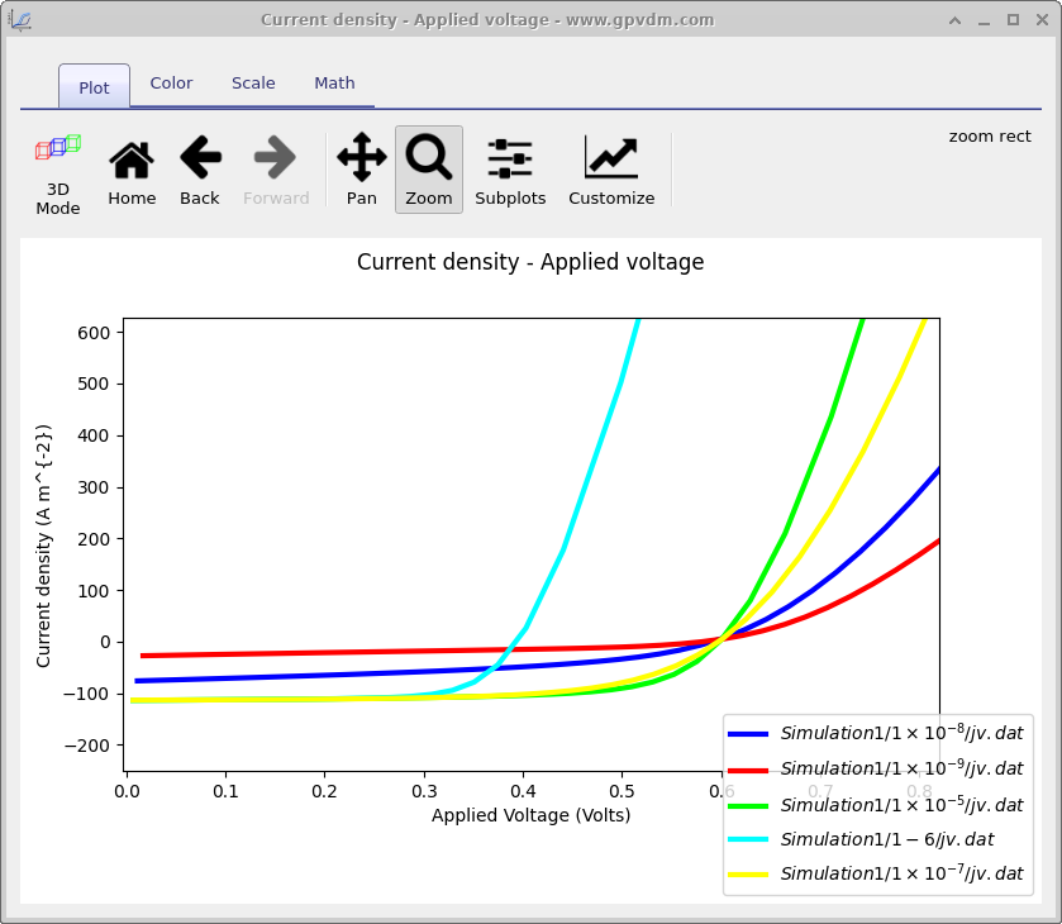
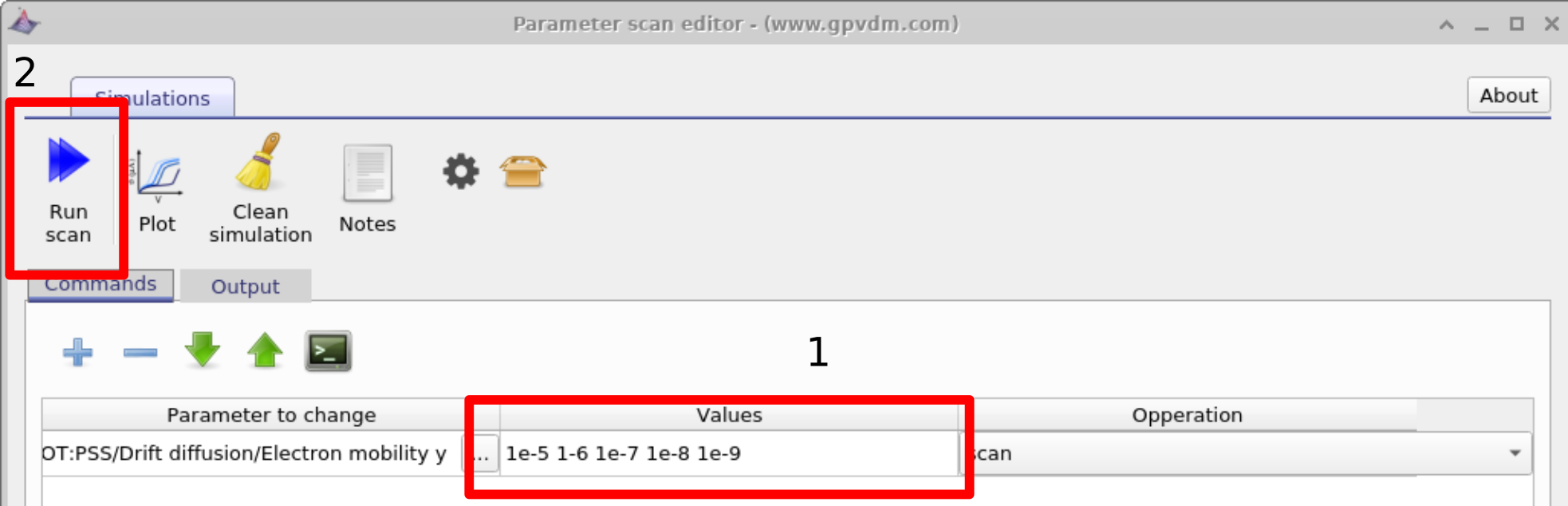
Em seguida insira os valores de mobilidade que deseja varrer, neste caso inseriremos 1e-5 1-6 1e-7 1e-8 1e-9 e então clique em run scan (veja figura 17.2 2). OghmaNano executará uma simulação em cada núcleo do seu computador até que todas as simulações sejam concluídas.
3. Visualizando os resultados da simulação
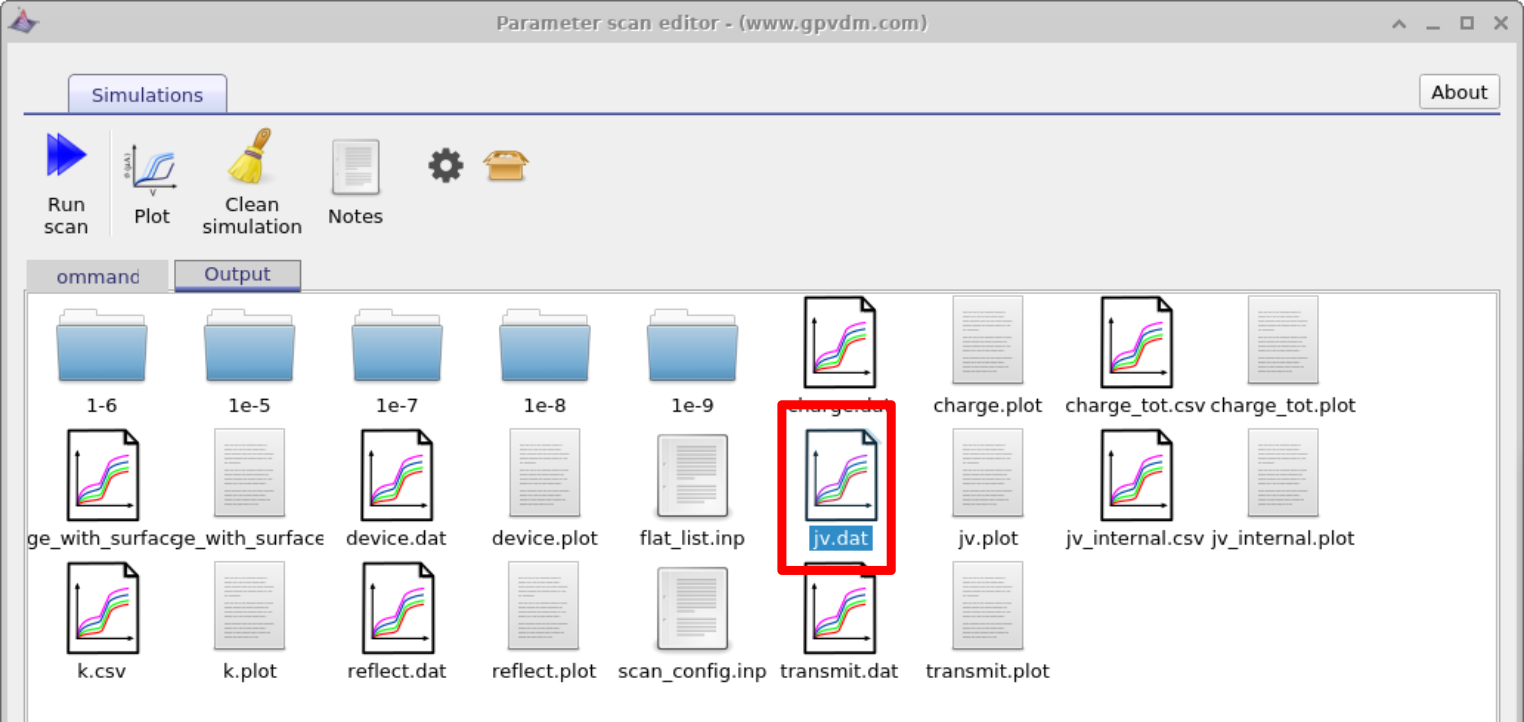
Para visualizar os resultados da simulação clique na aba output. Isso abrirá as saídas da simulação, veja figura 17.3. Você pode ver que um diretório foi criado para cada variável que varremos, ou seja 1e-5, 1e-6, 1e-7, 1e-8 e 1e-9. Se você olhar dentro de cada diretório ele será uma cópia exata do diretório base da simulação. Se você clicar duas vezes nos arquivos com curvas JV multicoloridas, veja a caixa vermelha na figura 17.3. OghmaNano irá automaticamente plotar todas as curvas de cada simulação em um único gráfico, veja figura 17.4.